Лактобактерии являются представителями естественной микрофлоры организма человека и животных и играют важную роль в поддержании колонизационной резистентности [1–2]. Они подавляют рост и размножение поступающих извне представителей посторонней микрофлоры, предотвращают их приживление. В организме человека лактобациллы появляются в первые дни после рождения и в течение всей его жизни присутствуют в кишечнике, препятствуя развитию гнилостных и патогенных микроорганизмов.
Развитие дисбактериоза в большинстве случаев связано с нарушением естественного состава микрофлоры кишечника. Представители рода Lactobacillus нашли свое применение в составе многочисленных лечебно-диетических кисломолочных продуктов и фармакопейных биопрепаратов [3–4].
Лактобактерии и продукты метаболизма широко используются для профилактики и лечения различных острых и хронических заболеваний пищеварительного тракта, способствуя восстановлению нормальной микрофлоры. Лактобактерии широко используются в пищевой промышленности в составе заквасок для приготовления кисломолочных продуктов (сыры, масла, йогурты), для хлебопечения (ржаной хлеб), для квашения овощей и засолки рыбы, для приготовления сухих и варено-копченых колбас [5].
Прежде чем использовать штаммы микроорганизмов для промышленного производства необходимо определить их разнообразные характеристики, в том числе и генетические, которые в отличие от культурально-морфологических более стабильны. Классическими методами внутривидового типирования микроорганизмов являются изучение морфологии, биохимические тесты и серологические реакции. Но вышеуказанные методы обладают существенными недостатками: они опираются на выявление вариабельных фенотипических признаков, относительная однородность которых определяет трудности во внутривидовой дифференциации микроорганизмов и не позволяет выявить различия между штаммами одного вида. Для повышения достоверности результатов при типировании штаммов лактобацилл целесообразно наряду с классическими использовать молекулярно-генетические методы исследования [6–8].
Молекулярно-генетические методы исследования позволяют не только провести внутриродовую дифференциацию лактобацилл на основании особенностей их геномов, но и дают возможность получить индивидуальные генотипические характеристики каждого штамма. Наиболее перспективными методами типирования штаммов лактобацилл, по нашему мнению, являются методы полимеразной цепной реакции (ПЦР). Одновременное применение нескольких методов ПЦР обеспечивает возможность генотипирования лактобацилл и позволяет решать задачи дифференциации видов и штаммов, входящих в состав пробиотических и производственных заквасок [9–10].
Материалы и методы исследования
Штаммы. В работе были использованы 3 штамма бактерий рода Lactobacillus, зарегистрированные в коллекции промышленных микроорганизмов РГП «Института микробиологии и вирусологии» КН МОН РК, по паспортным данным принадлежащих к Lactobacillus casei № 139, Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53H и 15 нуклеотидных последовательностей генов 16S rRNA молочнокислых бактерий, депонированные в базу данных NCBI.
Определение и анализ нуклеотидных последовательностей генов 16SrRNA. Геномную ДНК выделяли методом Kate Wilson [11]. Концентрацию ДНК измеряли спектрофотометрическим методом с использованием спектрофотометра Nano Drop 1000 при длине волны 260 нм, а также проводили качественную оценку ДНК электрофоретическим методом. Матрицы для секвенирования синтезировали с помощью ПЦР, используя универсальные праймеры 8f-5’-AgAgTTTgATCCTggCTCAg-3 и 806R-5’-ggACTACCAgggTATCTAAT-3 [12], что позволяло амплифицировать ген 16S rRNA почти полностью. Реакционная смесь (30 мкл) содержала 3 мкл 10х реакционного буфера (Fermentas), 2,5 мM MgCl2 , 0,2 мM каждого дезоксирибонуклеозидтрифосфата (дНТФ), по 10 пмоль каждого из праймеров, 1 единицу Taq – полимеразы Maxima Hot Start Taq DNA Polymerase (Fermentas) и 150 нг геномной ДНК в качестве матрицы. ПЦР проводили в термоциклере Mastercycler pro S (Eppendorf). Реакцию начинали инкубированием смеси при 95 °С в течение 7 минут, затем следовало 30 циклов, состоящих из инкубаций: 95 °С – 30 секунд, 55 °С – 40 секунд , 72 °С – 1 мин. Завершающую элонгацию проводили при 72 °С в течение 10 минут. Продукты амплификации разделяли в 1,5 % агарозном геле. Гели окрашивали этидиум бромидом. Электрофорез проводили в камере для горизонтального электрофореза Bio-RAD Basic и источником тока «Consort EV-243». В качестве электродного буфера использовали 1хТАЕ-буфер. Документирование полученных результатов проводили, используя систему документаций гелей Gel Doc. Размеры молекул анализируемых образцов ДНК определяли путем сопоставления их электрофоретической подвижности маркеров – фрагмент ДНК известной молекулярной массы. В качестве маркера молекулярных масс использовали O’GeneRuler™ 100bp Plus DNA Ladder производства (Fermentas). ПЦР продукты очищали от остатков олигонуклеотидов методом дефосфолирирования с помощью щелочной фосфатазы (SAP-shimp alkaline phosphatase) и эндонуклеазы I [13]. Секвенирование фрагментов гена 16S rRNA идентифицируемых бактерий проводили на автоматическом секвенаторе 3730хl DNA Analyzer (Applide Biosystems, США) с использованием набора Big Dye Terminator v3.1 Cycle Sequencing Kit (Applide Biosystems, США), придерживаясь рекомендаций производителя. Результаты секвенирования обрабатывали в программе SeqMan (Applide Biosystems). Поиск гомологичных нуклеотидных последовательностей генов 16S rRNA осуществляли с помощью программы BLAST в базе данных Gene Bank Национального центра биотехнологической информации США. Идентификация была осуществлена относительно инвентарных номеров Genе Bank первых трех нуклеотидных последовательностей, имеющих максимальное совпадение. Филогенетический анализ проводили с использованием программного обеспечения MEGA4 [14]. Выравнивание нуклеотидных последовательностей проводили, используя алгоритм ClustalW [15]. Для построения филогенетических деревьев использовали метод «объединения соседей» Neiighbor-Joining (NJ) [16].
Результаты исследования и их обсуждение
Филогенетический анализ нуклеотидных последовательностей генов 16S rRNA у рода Lactobacillus. В нашем исследовании генетическая идентификация 3 штаммов была осуществлена методом определения прямой нуклеотидной последовательности фрагмента 16S rRNA гена, с последующим сравнением нуклеотидной идентичности с последовательностями, депонированными в международной базе данных Gene Bank, а также построением филогенетических деревьев с нуклеотидными последовательностями референтных штаммов.
В результате выделения ДНК были получены образцы с высокой концентрацией ДНК от 80 до 150 нг/мкл, соотношение длин волн 260/280 в среднем составило 1,99. Методом ПЦР был амплифицирован фрагмент 16S rRNA гена, молекулярной массой размером около 800 п.н. Результаты амплификации образцов с отрицательным контролем отображены на рис. 1.
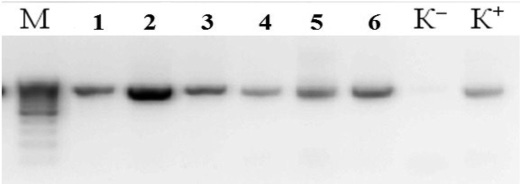
Рис. 1. Электрофорерограмма ПЦР продуктов амплификации фрагмента 16S rRNA гена ДНК: 1) – № 139, 2) – № 2, 3) – № 53Н; (М) – маркер молекулярной массы O’GeneRuler™ 100bp Plus DNA (Fermentas) (100 – 1000 п.н. от 100 – 1000 шаг 100 п.н.), (К-) – отрицательный контрольный образец; (К+) – положительный контрольный образец
Продукты ПЦР амплификации были использованы для определения нуклеотидной последовательности. Для исключения методической погрешности анализа 16S rRNA гена, дополнительно было проведено построение филогенетических деревьев (рис. 2, 3–4). После удаления последовательности праймеров в неперекрывающихся областях были получены нуклеотидные последовательности размером 650 п.н. При выравнивании было выявлено, что нуклеотидные последовательности фрагмента 16S rRNA гена референтных штаммов Lactobacillus casei (KJ739522.1), Lactobacillus plantarum (KM200717.1) и Lactobacillus pentosus (KF317899.1), а также Lactobacillus paracasei (KJ958418.1) и Lactobacillus casei (HG931728.1), Lactobacillus paracasei (KM009083.1) и Lactobacillus casei (KJ806307.1) имели размер 560 и 550 п.н. соответственно. В связи с этим для формирования однородной выборки размером 550 п.н. была удалена часть нуклеотидных последовательностей у исследуемых штаммов. Процент идентичности фрагментов нуклеотидных последовательностей 16S rRNA гена между Lactobacillus casei № 139 и Lactobacillus casei, Lactobacillus plantarum и Lactobacillus pentosus составил 100 %. У штаммов Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53Н и Lactobacillus paracasei и Lactobacillus casei также составил 100 %.

Рис. 2. Филогенетическое дерево, основанное на анализе структур фрагментов гена 16S rRNA, отражающее родственные связи штаммов молочнокислых бактерий рода Lactobacillus
Результаты филогенетического анализа последовательностей гена 16S rRNA у изучаемых штаммов представлены на филогенетическом дереве (рис. 2, 3–4), построенном в программе MEGA4, с использованием Neiighbor-Joining кластерного метода расчета генетических расстояний и bootstrap анализа, отражающего достоверность кластеризации.
Из представленных данных, по характеру последовательностей штаммы можно распределить в 2 кластера, один из которых составляет культуры Lactobacillus casei (KJ739522.1), Lactobacillus plantarum (KM200717.1) и Lactobacillus pentosus (KF317899.1), полные нуклеотидные последовательности которых характеризуются 100 %-м сходством. Второй кластер включает штамм Lactobacillus paraplantarum, сходство последовательностей гена 16S rRNA у которого составило 99–98 % (рис. 2). Как видно на рис. 2, при филогенетическом анализе фрагмента 16S rRNA гена штамм Lactobacillus casei № 139 был объединен в один кластер с Lactobacillus plantarum, Lactobacillus casei и Lactobacillus pentosus. При идентификации в Genе Bank штамм Lactobacillus casei № 139 находится на одной филогенетической ветви образуемой бактериями Lactobacillus casei, Lactobacillus plantarum и Lactobacillus pentosus что указывало на его принадлежность к одному из этих видов и исключало возможность отнесения к Lactobacillus casei. Разграничение видов Lactobacillus casei, Lactobacillus plantarum и Lactobacillus pentosus на основании результатов проведенного филогенетического анализа оказалось невозможным.
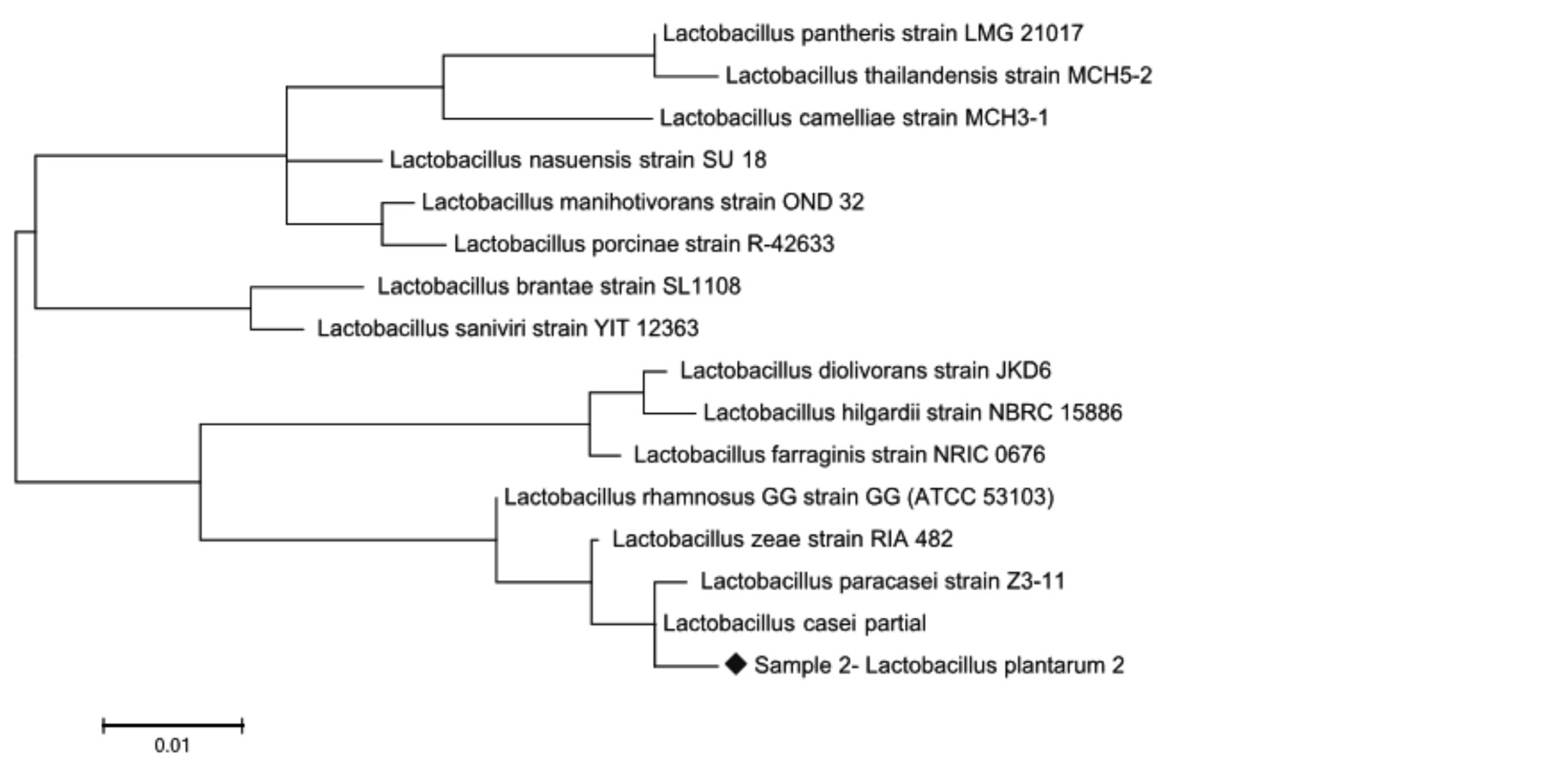
Рис. 3. Филогенетическое дерево, основанное на анализе структур фрагментов гена 16S rRNA, отражающее родственные связи штаммов молочнокислых бактерий рода Lactobacillus
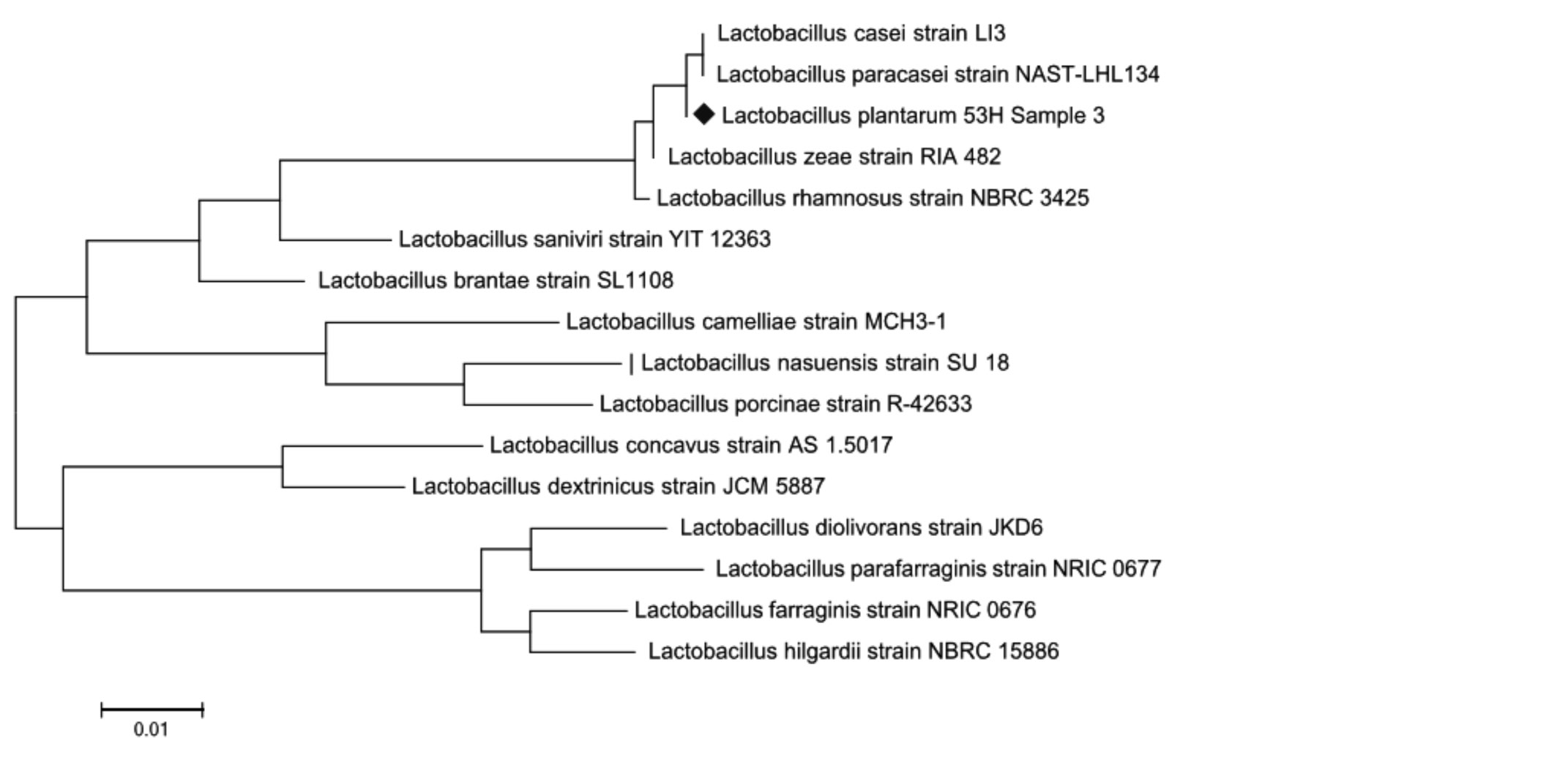
Рис. 4. Филогенетическое дерево, основанное на анализе структур фрагментов гена 16S rRNA, отражающее родственные связи штаммов молочнокислых бактерий рода Lactobacillus
Из представленных данных, по характеру последовательностей штаммы можно распределить в 2 кластера, один из которых составляет культуры Lactobacillus paracasei и Lactobacillus casei, нуклеотидные последовательности которых характеризуются 100 %-м сходством. Второй кластер включает штамм Lactobacillus zeae, сходство последовательностей гена 16S rRNA у которого составило 99–98 % (рис. 3–4). Как видно на рис. 3–4, при филогенетическом анализе фрагмента 16S rRNA гена штаммы Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53Н были объединены в один кластер с Lactobacillus casei-paracasei. При идентификации в Genе Bank штаммы Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53Н находятся на одной филогенетической ветви, образуемой бактериями Lactobacillus paracasei и Lactobacillus casei, что указывает на их принадлежность к одному из этих видов и исключает возможность отнесения к Lactobacillus plantarum. Разграничение видов Lactobacillus paracasei и Lactobacillus casei на основании результатов проведенного филогенетического анализа оказалось невозможным.
Причиной этого можно считать низкую вариабельность нуклеотидных последовательностей генов 16S rRNA. Коллекционные штаммы лактобацилл по результатам нашего анализа последовательностей их генов 16S rRNA были разделены на 2 группы. В первую группу Lactobacillus plantarum вошел штамм Lactobacillus casei № 139, видовая принадлежность которого не соответствует их исходным паспортным данным, составленным на основании традиционных микробиологических методов исследования. Ко второй группе Lactobacillus casei-paracasei отнесены штаммы Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53Н, у которых последовательность гена 16S rRNA также не соответствует видовому положению, указанному в паспортных данных.
В данном исследовании представлены результаты молекулярно-генетической идентификации трех штаммов молочнокислых бактерий на основе анализа нуклеотидных последовательностей 16S rRNA гена, выделенных из желудочно-кишечного тракта здоровых людей. Штаммы молочнокислых бактерий были просеквенированы и проанализированы.
Сравнение нуклеотидной последовательности генов 16SrRNA коллекционных штаммов с таковой международных баз данных позволило установить, что штаммы № 139, № 2 и № 53Н, идентифицированные ранее, как штаммы Lactobacillus casei № 139, Lactobacillus plantarum № 2 и Lactobacillus plantarum № 53Н, на самом деле относятся к Lactobacillus casei, Lactobacillus plantarum и Lactobacillus pentosus к группе Lactobacillus plantarum, а штаммы Lactobacillus paracasei и Lactobacillus casei – к группе Lactobacillus casei/paracasei.
Секвенирование гена 16S rRNA выявило высокий уровень гомологии с представителями рода Lactobacillus: штамм Lactobacillus casei № 139 – 100 % с Lactobacillus casei, Lactobacillus plantarum и Lactobacillus pentosus; а штамм Lactobacillus plantarum № 2 – 100 % с Lactobacillus paracasei и Lactobacillus casei. А также штамм, Lactobacillus plantarum № 53Н – 100 % с Lactobacillus paracasei и Lactobacillus casei.
Следовательно, сравнительный анализ нуклеотидных последовательностей трех штаммов молочнокислых бактерий показал их высокую идентичность.
Библиографическая ссылка
Джобулаева А.К., Джакибаева Г.Т., Кебекбаева К.М., Жаниязов Ж.А., Алимбетова А.В. ПРИМЕНЕНИЕ ПОЛИМЕРАЗНОЙ ЦЕПНОЙ РЕАКЦИИ ДЛЯ ИДЕНТИФИКАЦИИ КОЛЛЕКЦИОННЫХ КУЛЬТУР // Успехи современного естествознания. 2015. № 5. С. 121-125;URL: https://natural-sciences.ru/ru/article/view?id=35112 (дата обращения: 16.05.2026).



